5个回答
46
在scipy中,分布是以通用的方式编码的,涉及两个参数:位置和尺度。其中位置参数(
loc)将分布向左或向右移动,而尺度参数则压缩或拉伸分布。对于双参数对数正态分布,"均值"和"标准差"分别对应于log(scale)和shape(您可以让loc=0)。以下演示了如何拟合对数正态分布以找到感兴趣的两个参数。In [56]: import numpy as np
In [57]: from scipy import stats
In [58]: logsample = stats.norm.rvs(loc=10, scale=3, size=1000) # logsample ~ N(mu=10, sigma=3)
In [59]: sample = np.exp(logsample) # sample ~ lognormal(10, 3)
In [60]: shape, loc, scale = stats.lognorm.fit(sample, floc=0) # hold location to 0 while fitting
In [61]: shape, loc, scale
Out[61]: (2.9212650122639419, 0, 21318.029350592606)
In [62]: np.log(scale), shape # mu, sigma
Out[62]: (9.9673084420467362, 2.9212650122639419)
- ars
5
15
我刚刚花了一些时间研究这个问题,并想在这里记录一下:如果你想从lognorm.fit的三个返回值 ((shape, loc, scale)) 中获取概率密度 (在点x),你需要使用以下公式:
x = 1 / (shape*((x-loc)/scale)*sqrt(2*pi)) * exp(-1/2*(log((x-loc)/scale)/shape)**2) / scale
因此,给定方程式为(loc为µ,shape为σ,scale为α):
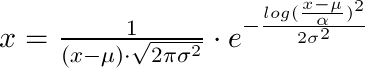
- Chronial
3
你的公式末尾为什么要除以(1/alpha)呢? - bioslime
2这不是我的公式,而是scipy的工作方式。我没有看到最后除以(1/α},所以我会假设您说的是除以
scale - 如果我误解了,请纠正我。我一段时间前看过这段代码,但如果我记得正确,那就是对每种分布都要做的事情。但请注意,在开始时还有另一个scale,它们互相抵消了(正如您在方程中看到的那样)。 - Chronial这两个比例尺相互抵消。所以最好使用它:
(np.exp((-1/2)*(np.log((x-loc)/scale)/shape)*2))/(shape(x-loc)np.sqrt(2np.pi)) - Gouz
2
我认为这会有所帮助。 我长时间以来一直在寻找同样的问题,并最终找到了解决我的问题的方法。 在我的情况下,我试图使用
在下面的代码中,我从平均值和标准差参数中解释如何使用scipy.stats.norm模块生成正态分布的数据样本。使用这些数据,我适配了正常模型(
原始模型产生的数据,拟合和由(mu-sigma)对产生的数据在图表中进行了比较。
在代码的下一部分,我使用普通数据生成对数正态分布的样本。为此,请注意对数正态样本将是原始样本的指数。因此,指数样本的均值和标准差将分别为(
我将生成的数据拟合到一个
要从原始数据(x)的均值和标准差生成对数正态模型,代码如下:
scipy.stats.lognorm模块将一些数据适配到对数正态分布上。 然而,当我最终得到模型参数时,我无法找到一种方法使用y数据的平均值和标准差复制我的结果。在下面的代码中,我从平均值和标准差参数中解释如何使用scipy.stats.norm模块生成正态分布的数据样本。使用这些数据,我适配了正常模型(
norm_dist_fitted),并创建了一个使用从数据中提取的平均值和标准偏差(mu,sigma)的正常模型。原始模型产生的数据,拟合和由(mu-sigma)对产生的数据在图表中进行了比较。
在代码的下一部分,我使用普通数据生成对数正态分布的样本。为此,请注意对数正态样本将是原始样本的指数。因此,指数样本的均值和标准差将分别为(
exp(mu) 和 exp(sigma))。我将生成的数据拟合到一个
lognormal模型中(由于我的样本的对数(exp(x)) 是正态分布的,并且遵循对数正态模型的假设)。要从原始数据(x)的均值和标准差生成对数正态模型,代码如下:
lognorm_dist = scipy.stats.lognorm(s=sigma, loc=0, scale=np.exp(mu))
然而,如果你的数据已经在指数空间(exp(x))中,则必须使用:
muX = np.mean(np.log(x))
sigmaX = np.std(np.log(x))
scipy.stats.lognorm(s=sigmaX, loc=0, scale=muX)
{{链接1: 图2}}
import scipy
import matplotlib.pyplot as plt
import seaborn as sns
import numpy as np
mu = 10 # Mean of sample !!! Make sure your data is positive for the lognormal example
sigma = 1.5 # Standard deviation of sample
N = 2000 # Number of samples
norm_dist = scipy.stats.norm(loc=mu, scale=sigma) # Create Random Process
x = norm_dist.rvs(size=N) # Generate samples
# Fit normal
fitting_params = scipy.stats.norm.fit(x)
norm_dist_fitted = scipy.stats.norm(*fitting_params)
t = np.linspace(np.min(x), np.max(x), 100)
# Plot normals
f, ax = plt.subplots(1, sharex='col', figsize=(10, 5))
sns.distplot(x, ax=ax, norm_hist=True, kde=False, label='Data X~N(mu={0:.1f}, sigma={1:.1f})'.format(mu, sigma))
ax.plot(t, norm_dist_fitted.pdf(t), lw=2, color='r',
label='Fitted Model X~N(mu={0:.1f}, sigma={1:.1f})'.format(norm_dist_fitted.mean(), norm_dist_fitted.std()))
ax.plot(t, norm_dist.pdf(t), lw=2, color='g', ls=':',
label='Original Model X~N(mu={0:.1f}, sigma={1:.1f})'.format(norm_dist.mean(), norm_dist.std()))
ax.legend(loc='lower right')
plt.show()
# The lognormal model fits to a variable whose log is normal
# We create our variable whose log is normal 'exponenciating' the previous variable
x_exp = np.exp(x)
mu_exp = np.exp(mu)
sigma_exp = np.exp(sigma)
fitting_params_lognormal = scipy.stats.lognorm.fit(x_exp, floc=0, scale=mu_exp)
lognorm_dist_fitted = scipy.stats.lognorm(*fitting_params_lognormal)
t = np.linspace(np.min(x_exp), np.max(x_exp), 100)
# Here is the magic I was looking for a long long time
lognorm_dist = scipy.stats.lognorm(s=sigma, loc=0, scale=np.exp(mu))
# The trick is to understand these two things:
# 1. If the EXP of a variable is NORMAL with MU and STD -> EXP(X) ~ scipy.stats.lognorm(s=sigma, loc=0, scale=np.exp(mu))
# 2. If your variable (x) HAS THE FORM of a LOGNORMAL, the model will be scipy.stats.lognorm(s=sigmaX, loc=0, scale=muX)
# with:
# - muX = np.mean(np.log(x))
# - sigmaX = np.std(np.log(x))
# Plot lognormals
f, ax = plt.subplots(1, sharex='col', figsize=(10, 5))
sns.distplot(x_exp, ax=ax, norm_hist=True, kde=False,
label='Data exp(X)~N(mu={0:.1f}, sigma={1:.1f})\n X~LogNorm(mu={0:.1f}, sigma={1:.1f})'.format(mu, sigma))
ax.plot(t, lognorm_dist_fitted.pdf(t), lw=2, color='r',
label='Fitted Model X~LogNorm(mu={0:.1f}, sigma={1:.1f})'.format(lognorm_dist_fitted.mean(), lognorm_dist_fitted.std()))
ax.plot(t, lognorm_dist.pdf(t), lw=2, color='g', ls=':',
label='Original Model X~LogNorm(mu={0:.1f}, sigma={1:.1f})'.format(lognorm_dist.mean(), lognorm_dist.std()))
ax.legend(loc='lower right')
plt.show()
- nenetto
2
请在回答中提供一些解释。 - Collin Barrett
@CollinM.Barrett 完成了! :D 希望一切都好 :D - nenetto
0
首先,loc 不是分布的简单线性偏移,实际上,loc 有其自身的统计意义,它表示样本减去 loc 后会得到一个“标准化”的对数正态分布,其下限为零,这一点非常重要。
因此,当您指定“loc”或“floc”时,实际上您施加了一种非常强的假设,即您假定这些样本具有下限,并且下限“恰好”是“loc”的值。因此,scipy 使用不同的算法进行拟合,即:
如果您提供 loc 信息,则 scipy 将采用最大似然方法计算拟合参数;如果没有,则将使用数值解算器。
此外,您可以查看代码: 在 scipy 包 stats/_continuous_distns.py 第 3889 行。如下所示:
def fit(self, data, *args, **kwds):
floc = kwds.get('floc', None)
if floc is None:
# loc is not fixed. Use the default fit method.
return super(lognorm_gen, self).fit(data, *args, **kwds)
f0 = (kwds.get('f0', None) or kwds.get('fs', None) or
kwds.get('fix_s', None))
fscale = kwds.get('fscale', None)
if len(args) > 1:
raise TypeError("Too many input arguments.")
for name in ['f0', 'fs', 'fix_s', 'floc', 'fscale', 'loc', 'scale',
'optimizer']:
kwds.pop(name, None)
if kwds:
raise TypeError("Unknown arguments: %s." % kwds)
# Special case: loc is fixed. Use the maximum likelihood formulas
# instead of the numerical solver.
此外,来自
R社区的人可能会想知道为什么python的输出与R不同。实际上,我不赞成将R用作“参考”,它只是一种软件,不同的软件有不同风味的算法。例如,
R的输出如下所示并非错误,Python或其他软件(如Fortran)使用完全不同的算法:round(3.5)
[1] 4
round(2.5)
[1] 2
- Chao Sun
-1
有助于我的一点是将位置和比例作为参数化考虑。
与标准对数正态分布中使用x不同,您可以更改为x'=(x-位置)/比例
然后概率密度函数F(x')=(1/比例)F((x-位置)/比例))
更多信息请参见链接https://en.wikipedia.org/wiki/Location%E2%80%93scale_family
- Mateus Kinasz
网页内容由stack overflow 提供, 点击上面的可以查看英文原文,
原文链接
原文链接
mu = log(scale)(显然是正确的) - Jakub M.