2个回答
15
计算密度估计曲线下的面积并不困难。这里是一个可重复的示例。
假设我们有一些观测数据x,为了简单起见,我们假设这些数据是正态分布的:
set.seed(0)
x <- rnorm(1000)
我们进行密度估计(带有一些自定义,参见?density):
d <- density.default(x, n = 512, cut = 3)
str(d)
# List of 7
# $ x : num [1:512] -3.91 -3.9 -3.88 -3.87 -3.85 ...
# $ y : num [1:512] 2.23e-05 2.74e-05 3.35e-05 4.07e-05 4.93e-05 ...
# ... truncated ...
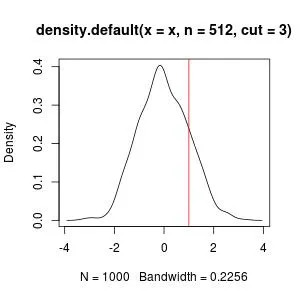
我们想要计算曲线右侧 x = 1 的面积:
plot(d); abline(v = 1, col = 2)
数学上,这是在[1, Inf]上对估计的密度曲线进行数值积分。
估计的密度曲线以离散格式存储在d$x和d$y中:
xx <- d$x ## 512 evenly spaced points on [min(x) - 3 * d$bw, max(x) + 3 * d$bw]
dx <- xx[2L] - xx[1L] ## spacing / bin size
yy <- d$y ## 512 density values for `xx`
数值积分有两种方法。
方法1: 黎曼和
估计密度曲线下的面积为:
C <- sum(yy) * dx ## sum(yy * dx)
# [1] 1.000976
由于黎曼和只是一种近似方法,因此与1(总概率)略有偏差。 我们将这个C值称为“归一化常数”。
[1, Inf]上的数值积分可以近似为
p.unscaled <- sum(yy[xx >= 1]) * dx
# [1] 0.1691366
应进一步通过C进行缩放,以进行适当的概率估计:
p.scaled <- p.unscaled / C
# [1] 0.1689718
由于我们知道模拟的 x 的真实密度,因此我们可以将这个估计值与真实值进行比较:
pnorm(x0, lower.tail = FALSE)
# [1] 0.1586553
方法2:梯形公式
对 (xx, yy) 进行线性插值,然后对该线性插值进行数值积分,其结果相当接近。
f <- approxfun(xx, yy)
C <- integrate(f, min(xx), max(xx))$value
p.unscaled <- integrate(f, 1, max(xx))$value
p.scaled <- p.unscaled / C
#[1] 0.1687369
关于Robin的答案
这个答案是合法的,但可能是在作弊。OP的问题始于密度估计,但是该答案完全绕过了它。如果允许这样做,为什么不简单地这样做呢?
set.seed(0)
x <- rnorm(1000)
mean(x > 1)
#[1] 0.163
- Zheyuan Li
2
我理解你在回复我的答案时的观点,我认为我们对问题的阅读方式不同。由于OP使用density()来获取密度估计值,因此他们将拥有原始数据。在这种情况下,我不认为我的答案是作弊。他们确实可以绕过对密度估计曲线进行积分。我仍在学习中,如果我错了,请纠正我。 - Robin
@李哲源 当我们必须计算phi的平方时该怎么办?我的意思是如何计算相同积分但是针对平方phi。 - Z B
5
基于 R 的经验累积分布函数
ecdf() 非常容易使用。以李哲源的例子为例...#Reproducible sample data
set.seed(0)
x <- rnorm(1000)
#Create empirical cumulative distribution function from sample data
d_fun <- ecdf (x)
#Assume a value for the "red vertical line"
x0 <- 1
#Area under curve less than, equal to x0
d_fun(x0)
# [1] 0.837
#Area under curve greater than x0
1 - d_fun(x0)
# [1] 0.163
关于李哲源对我的回答的回应。 他们的答案假设你只有密度估计曲线。 而我的答案假设您拥有原始数据,这适用于OP的问题,因为他们使用density()来获得密度估计曲线。
- Robin
网页内容由stack overflow 提供, 点击上面的可以查看英文原文,
原文链接
原文链接