我有一个关于scipy中使用的拟合算法的问题。在我的程序中,我有一组x和y数据点,只有y的误差,并且想要拟合一个函数。
f(x) = (a[0] - a[1])/(1+np.exp(x-a[2])/a[3]) + a[1]
对它进行操作。
问题在于,我在参数上得到了荒谬的高误差,并且使用两个拟合scipy拟合例程scipy.odr.ODR(使用最小二乘算法)和scipy.optimize时得到不同的值和拟合参数的误差。以下是我的示例:
使用scipy.odr.ODR进行拟合,fit_type=2
Beta: [ 11.96765963 68.98892582 100.20926023 0.60793377]
Beta Std Error: [ 4.67560801e-01 3.37133614e+00 8.06031988e+04 4.90014367e+04]
Beta Covariance: [[ 3.49790629e-02 1.14441187e-02 -1.92963671e+02 1.17312104e+02]
[ 1.14441187e-02 1.81859542e+00 -5.93424196e+03 3.60765567e+03]
[ -1.92963671e+02 -5.93424196e+03 1.03952883e+09 -6.31965068e+08]
[ 1.17312104e+02 3.60765567e+03 -6.31965068e+08 3.84193143e+08]]
Residual Variance: 6.24982731975
Inverse Condition #: 1.61472215874e-08
Reason(s) for Halting:
Sum of squares convergence
然后使用scipy.optimize.leastsquares进行拟合:
使用scipy.optimize.leastsq进行拟合
beta: [ 11.9671859 68.98445306 99.43252045 1.32131099]
Beta Std Error: [0.195503 1.384838 34.891521 45.950556]
Beta Covariance: [[ 3.82214235e-02 -1.05423284e-02 -1.99742825e+00 2.63681933e+00]
[ -1.05423284e-02 1.91777505e+00 1.27300761e+01 -1.67054172e+01]
[ -1.99742825e+00 1.27300761e+01 1.21741826e+03 -1.60328181e+03]
[ 2.63681933e+00 -1.67054172e+01 -1.60328181e+03 2.11145361e+03]]
Residual Variance: 6.24982904455 (calulated by me)
我的观点是第三个拟合参数:结果如下
scipy.odr.ODR,fit_type=2:
C = 100.209 +/- 80600
scipy.optimize.leastsq:
C = 99.432 +/- 12.730
我不知道为什么第一个误差要高得多。更好的是:如果我将完全相同的数据点和误差放入Origin 9中,我会得到 C = x0 = 99,41849 +/- 0,20283
并且将完全相同的数据放入c++ ROOT Cern C = 99.85+/- 1.373
即使我在ROOT和Python中使用了完全相同的初始变量,Origin也不需要任何变量。
您有任何线索为什么会发生这种情况以及哪个结果最好吗?
我已经在pastebin上为您添加了代码:
感谢您的帮助!
编辑:这是与SirJohnFranklins帖子相关的情节: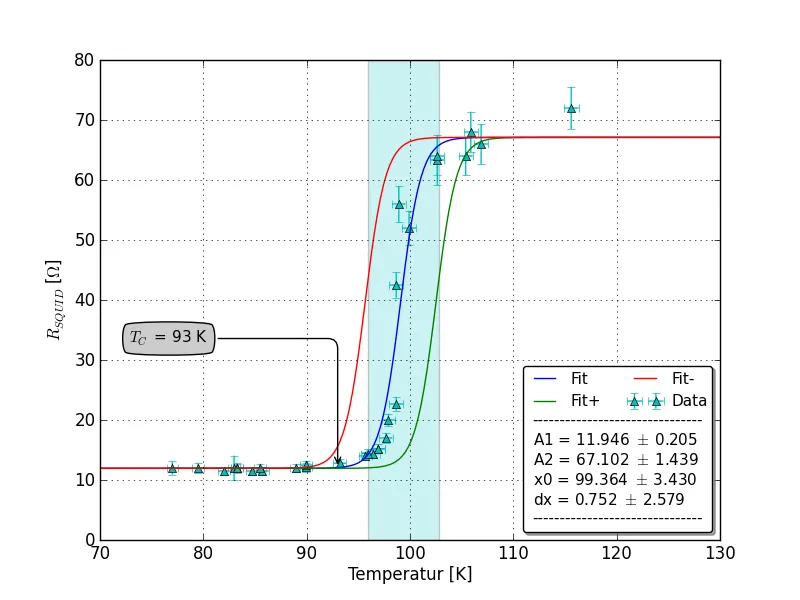
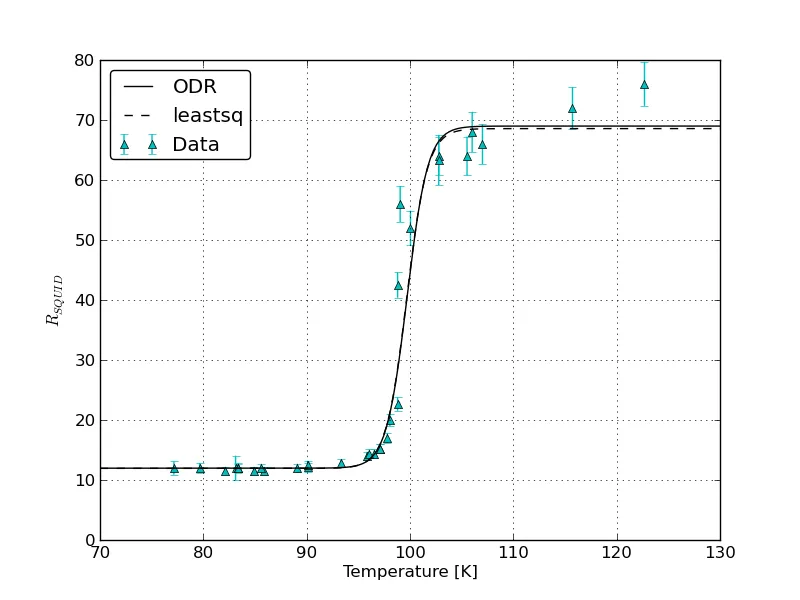
scipy.odr和(2)带有x和y误差的ROOT所得到的拟合和误差?此外,由于x和y误差是用不同的单位测量的,ROOT如何确定相对加权给予它们?在scipy.odr中,sx和sy通过将1.0除以它们的平方来转换为权重 -ROOT是否也这样做? - ali_m