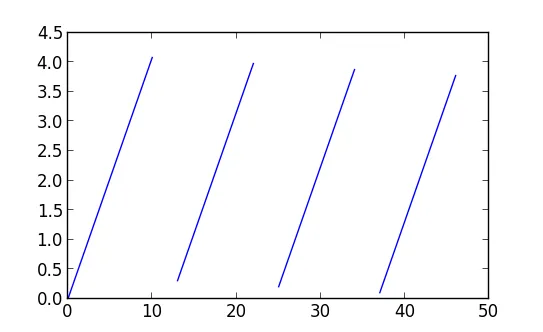
我有一些物体在闭合边界的走廊内移动的数据。 将轨迹绘制出来会得到一个锯齿形轨迹。
我想知道如何防止plot()连接粒子回到起点的点,就像图片上面部分那样,但没有"."
我最初的想法是找到numpy数组a[:-1]-a[1:]变为正的索引,然后从0到该索引进行绘图。 但是我怎样才能获得a[:-1]-a[1:]的第一次正值元素的索引呢? 可能还有其他的想法。
我有一些物体在闭合边界的走廊内移动的数据。 将轨迹绘制出来会得到一个锯齿形轨迹。

我想知道如何防止plot()连接粒子回到起点的点,就像图片上面部分那样,但没有"."
我最初的想法是找到numpy数组a[:-1]-a[1:]变为正的索引,然后从0到该索引进行绘图。 但是我怎样才能获得a[:-1]-a[1:]的第一次正值元素的索引呢? 可能还有其他的想法。
我会选择不同的方法。首先,我不会通过查看导数的符号来确定跳跃点,因为运动可能向上或向下,甚至可能具有一些周期性。我会查看那些具有最大导数的点。
其次,一个优雅的方法在绘制线条时具有突破点是在每个跳跃点掩盖一个值。然后Matplotlib将自动创建线段。我的代码如下:
import pylab as plt
import numpy as np
xs = np.linspace(0., 100., 1000.)
data = (xs*0.03 + np.sin(xs) * 0.1) % 1
plt.subplot(2,1,1)
plt.plot(xs, data, "r-")
#Make a masked array with jump points masked
abs_d_data = np.abs(np.diff(data))
mask = np.hstack([ abs_d_data > abs_d_data.mean()+3*abs_d_data.std(), [False]])
masked_data = np.ma.MaskedArray(data, mask)
plt.subplot(2,1,2)
plt.plot(xs, masked_data, "b-")
plt.show()
结果如下图所示:
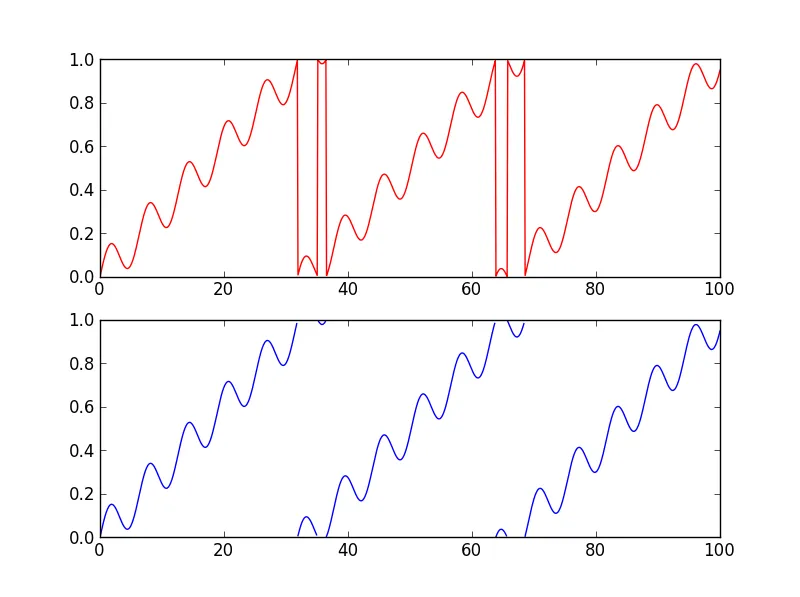
当然,缺点是每次断开连接都会损失一个点数-但是根据你所拥有的采样率,我想你可以用更简单的代码来交换这一点。
>>> import numpy as np
>>> a = np.linspace(0, 10, 50) % 5
>>> a = np.linspace(0, 10, 50) % 5 # some sample data
>>> np.nonzero(np.diff(a) < 0)[0] + 1
array([25, 49])
>>> a[24:27]
array([ 4.89795918, 0.10204082, 0.30612245])
>>> a[48:]
array([ 4.79591837, 0. ])
>>>
np.diff(a) 函数计算数组 a 的离散差分,而 np.nonzero 函数则用于找出条件 np.diff(a) < 0 不成立的位置,即粒子向下移动的位置。
np.linspace(0., 100., 100)与原始np.linspace(0., 100., 1000)相比,则这一点非常重要。曲线的x位置进行线性插值。封装成一个函数如下:import numpy as np
def periodic2plot(x, y, period=np.pi*2.):
indexes = np.argwhere(np.abs(np.diff(y))>.5*period).flatten()
index_shift = 0
for i in indexes:
i += index_shift
index_shift += 3 # in every loop it adds 3 elements
if y[i] > .5*period:
x_transit = np.interp(period, np.unwrap(y[i:i+2], period=period), x[i:i+2])
add = np.ma.array([ period, 0., 0.], mask=[0,1,0])
else:
# interpolate needs sorted xp = np.unwrap(y[i:i+2], period=period)
x_transit = np.interp(0, np.unwrap(y[i:i+2], period=period)[::-1], x[i:i+2][::-1])
add = np.ma.array([ 0., 0., period], mask=[0,1,0])
x_add = np.ma.array([x_transit]*3, mask=[0,1,0])
x = np.ma.hstack((x[:i+1], x_add, x[i+1:]))
y = np.ma.hstack((y[:i+1], add, y[i+1:]))
return x, y
import matplotlib.pyplot as plt
x = np.linspace(0., 100., 100)
y = (x*0.03 + np.sin(x) * 0.1) % 1
#Thorsten Kranz: Make a masked array with jump points masked
abs_d_data = np.abs(np.diff(y))
mask = np.hstack([np.abs(np.diff(y))>.5, [False]])
masked_y = np.ma.MaskedArray(y, mask)
# Plot
plt.figure()
plt.plot(*periodic2plot(x, y, period=1), label='This answer')
plt.plot(x, masked_y, label='Thorsten Kranz')
plt.autoscale(enable=True, axis='both', tight=True)
plt.legend(loc=1)
plt.tight_layout()
a变号时按段绘制的快速方法:import numpy as np
a = np.linspace(0, 20, 50) % 5 # similar to Micheal's sample data
x = np.arange(50) # x scale
indices = np.where(np.diff(a) < 0)[0] + 1 # the same as Micheal's np.nonzero
for n, i in enumerate(indices):
if n == 0:
plot(x[:i], a[:i], 'b-')
else:
plot(x[indices[n - 1]:i], a[indices[n - 1]:i], 'b-')