我正在尝试生成一个热力图,其中像素值由两个独立的二维高斯分布控制。让它们分别为Kernel1(muX1,muY1,sigmaX1,sigmaY1)和Kernel2(muX2,muY2,sigmaX2,sigmaY2)。更具体地说,每个内核的长度是其标准偏差的三倍。第一个内核具有sigmaX1 = sigmaY1,而第二个内核具有sigmaX2 < sigmaY2。两个内核的协方差矩阵都是对角线矩阵(X和Y是独立的)。Kernel1通常完全包含在Kernel2中。
我尝试了以下两种方法,但结果都不理想。能否给我一些建议?
方法1:
遍历地图上的所有像素值对(i,j),并计算给定I(i,j)= P(i,j | Kernel1,Kernel2)的I(i,j)的值= 1-(1-P(i,j | Kernel1))*(1-P(i,j | Kernel2))。然后我得到了以下结果,在平滑性方面效果良好。但它在我的电脑上运行需要10秒钟,速度太慢了。
代码:
我尝试了以下两种方法,但结果都不理想。能否给我一些建议?
方法1:
遍历地图上的所有像素值对(i,j),并计算给定I(i,j)= P(i,j | Kernel1,Kernel2)的I(i,j)的值= 1-(1-P(i,j | Kernel1))*(1-P(i,j | Kernel2))。然后我得到了以下结果,在平滑性方面效果良好。但它在我的电脑上运行需要10秒钟,速度太慢了。
代码:
def genDensityBox(self, height, width, muY1, muX1, muY2, muX2, sigmaK1, sigmaY2, sigmaX2):
densityBox = np.zeros((height, width))
for y in range(height):
for x in range(width):
densityBox[y, x] += 1. - (1. - multivariateNormal(y, x, muY1, muX1, sigmaK1, sigmaK1)) * (1. - multivariateNormal(y, x, muY2, muX2, sigmaY2, sigmaX2))
return densityBox
def multivariateNormal(y, x, muY, muX, sigmaY, sigmaX):
return norm.pdf(y, loc=muY, scale=sigmaY) * norm.pdf(x, loc=muX, scale=sigmaX)
第二种方法:
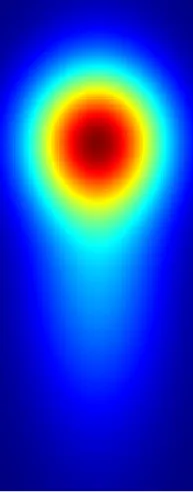
分别生成两个与两个核对应的图像,然后使用特定的alpha值将它们混合在一起。每个图像都是通过取两个一维高斯滤波器的外积来生成的。然后我得到了以下非常粗糙的结果。但这种方法的优点是由于在两个向量之间使用外积,所以速度非常快。
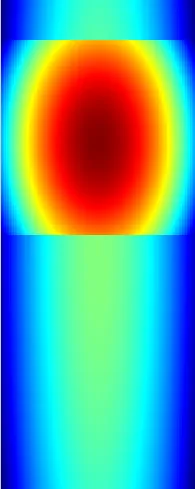
由于第一种方法很慢而第二种方法很粗糙,我正在尝试找到一种新的方法,既可以实现良好的平滑度,又可以同时具有低时间复杂度。有人能给我一些帮助吗?
谢谢!
对于第二种方法,可以像这里提到的那样轻松生成2D高斯地图:here:
def gkern(self, sigmaY, sigmaX, yKernelLen, xKernelLen, nsigma=3):
"""Returns a 2D Gaussian kernel array."""
yInterval = (2*nsigma+1.)/(yKernelLen)
yRow = np.linspace(-nsigma-yInterval/2.,nsigma+yInterval/2.,yKernelLen + 1)
kernelY = np.diff(st.norm.cdf(yRow, 0, sigmaY))
xInterval = (2*nsigma+1.)/(xKernelLen)
xRow = np.linspace(-nsigma-xInterval/2.,nsigma+xInterval/2.,xKernelLen + 1)
kernelX = np.diff(st.norm.cdf(xRow, 0, sigmaX))
kernelRaw = np.sqrt(np.outer(kernelY, kernelX))
kernel = kernelRaw / (kernelRaw.sum())
return kernel
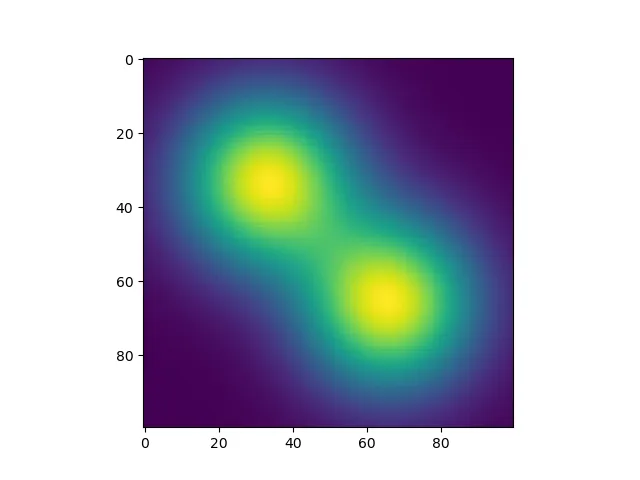
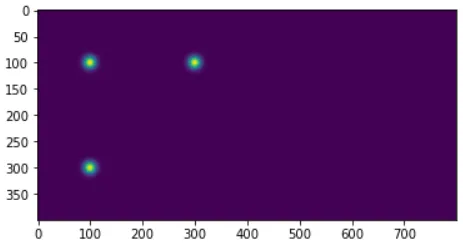
plt.imshow(img, origin='lower')来修复这个问题。 - undefined