我有一个由Python中的networkX创建的有向图G,每条边都是双向的。我有一定的节点列表,并且我正在尝试找到这些节点之间的连通组件。下面我创建了一个示例数据集(我正在处理的实际图形要大得多)。
import networkx as nx
G = nx.DiGraph()
nodeList = range(1,10)
for i in range (0,len(nodeList)):
G.add_node(nodeList[i])
o_nodes = [1,1,2,3,3,3,3,4,4,5,5,6,7,7,8,9,9,10]
d_nodes = [8,3,3,1,7,2,4,5,3,4,6,5,3,9,1,7,10,9]
for i in range(0, len(o_nodes)):
G.add_edge(o_nodes[i], d_nodes[i])
nx.draw(G, with_labels = True)
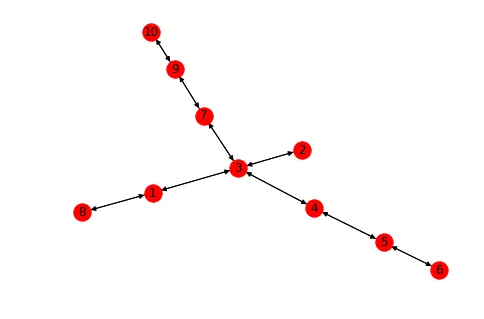
假设我有一个节点列表,selectNodeList = [1,2,5,6,7,8,9,10],我需要找到这些节点之间的连通分量。因此,结果应该是像 [8,1], [7,9,10], [2], [5,6] 这样的东西。我希望得到最少的组件数量,以覆盖选择节点列表中的所有节点。
我尝试使用一个for循环和if nx.shortest_path_length(G, source = selectNodeList[i], target = selectNodeList[j]) == 1:,然后将结果附加到列表中,以获取每个节点的直接邻居,但是我不确定如何进一步获取邻居,以及如何创建可读的输出。
编辑:这是我在上面提到的代码。我不愿意添加它,因为它没有完全完成。我的思路是首先获取两个直接相邻的节点,然后搜索另一个节点,该节点也是其中一个节点的直接邻居,以此类推。但是,这样做不能输出完全没有连接的节点,并且会导致重复连接的节点列表(例如[1 8 1 8 1 8 5 6 5 6 ...])。对我来说,一个问题是我不知道如何处理创建不同维度输出的问题,以及如何在不创建大量for循环的情况下解决问题。
connected = []
for i in range(0,34):
for j in range (1,34):
if nx.shortest_path_length(G, source = selectNodeList[i], target = selectNodeList[j]) == 1:
connected.append(selectNodeList[i])
connected.append(selectNodeList[j])
for k in range(2,34):
if nx.shortest_path_length(G, source = selectNodeList[j], target = selectNodeList[k]) == 1:
connected.append(selectNodeList[k])
for l in range (3,34):
if nx.shortest_path_length(G, source = selectNodeList[k], target = selectNodeList[l]) == 1:
connected.append(selectNodeList[l])
for m in range(4,34):
if nx.shortest_path_length(G, source = selectNodeList[l], target = selectNodeList[m]) == 1:
connected.append(selectNodeList[m])
nx.connected_components不起作用,因为图是有向的。我已经尝试使用nx.strongly_connected_components,但是结果是整个图的所有节点编号的列表,而不仅仅是节点列表中的节点编号。我不确定原因。 - Zasuconnected= [list(c) for c in nx.connected_components(G)],但这会导致列表中包含图形的所有节点编号。 - Zasu