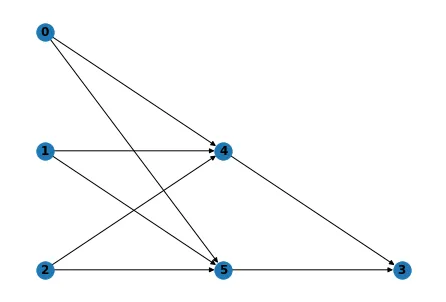
所谓“标准格式”,是指将输入和输出节点分别放在自己的单独行中,而将其他所有隐藏节点都放在它们之间。如下图所示,我的输入节点是0、1和2,输出节点是3,隐藏节点是4和5。这是我能得到的最好看的网络图。我试图避免使用Keras,因为在Anaconda中尝试让它起作用一直是个大问题。
我相信,如果我知道用于显示神经网络的“标准格式”图形的名称,那么这将会更容易。
请告诉我是否有我错过的用于执行此任务的包。
以下是我现在显示网络的方法:

图形的代码:
import networkx as nx
G = nx.MultiDiGraph()
ed = N2.dna.get_conns(weight=True)
G.add_weighted_edges_from(ed)
nx.draw_planar(G,with_labels=True,font_weight='bold')
ed
Out[32]:
[[0, 3, -1],
[1, 3, -1],
[2, 3, -1],
[0, 4, -1],
[4, 5, -1],
[5, 3, 100],
[2, 4, 10]]